SARS-CoV2 diagnostiek voor een breder publiek
Vanaf 1 juni 2020 mag iedereen zich laten testen op SARS-CoV2 (Coronavirus) en is er dus behoefte aan meer testcapaciteit, vereenvoudiging van monsterafname (en logistiek), testen en rapportage. Daarbij is het essentieel het proces zoveel mogelijk te automatiseren en het uitleessysteem te vergemakkelijken.
Onderdeel van:
Wat houdt het project in?
Verbeterde moleculaire diagnostiek procesketen en user-friendly IT.
Om het coronavirus snel te kunnen detecteren is moleculaire diagnostiek de enige optie. In vitro-diagnostiek, waaronder Corona-virusdiagnostiek valt, zal in 2022 uitgegroeid zijn tot de grootste tak van sport met voorspellingen voor sales tot wel $70.8 biljoen. Er moet snel op worden ingezet om hierin mee te kunnen gaan.
Het huidige meetproces opgesteld door RIVM kent vier stappen:
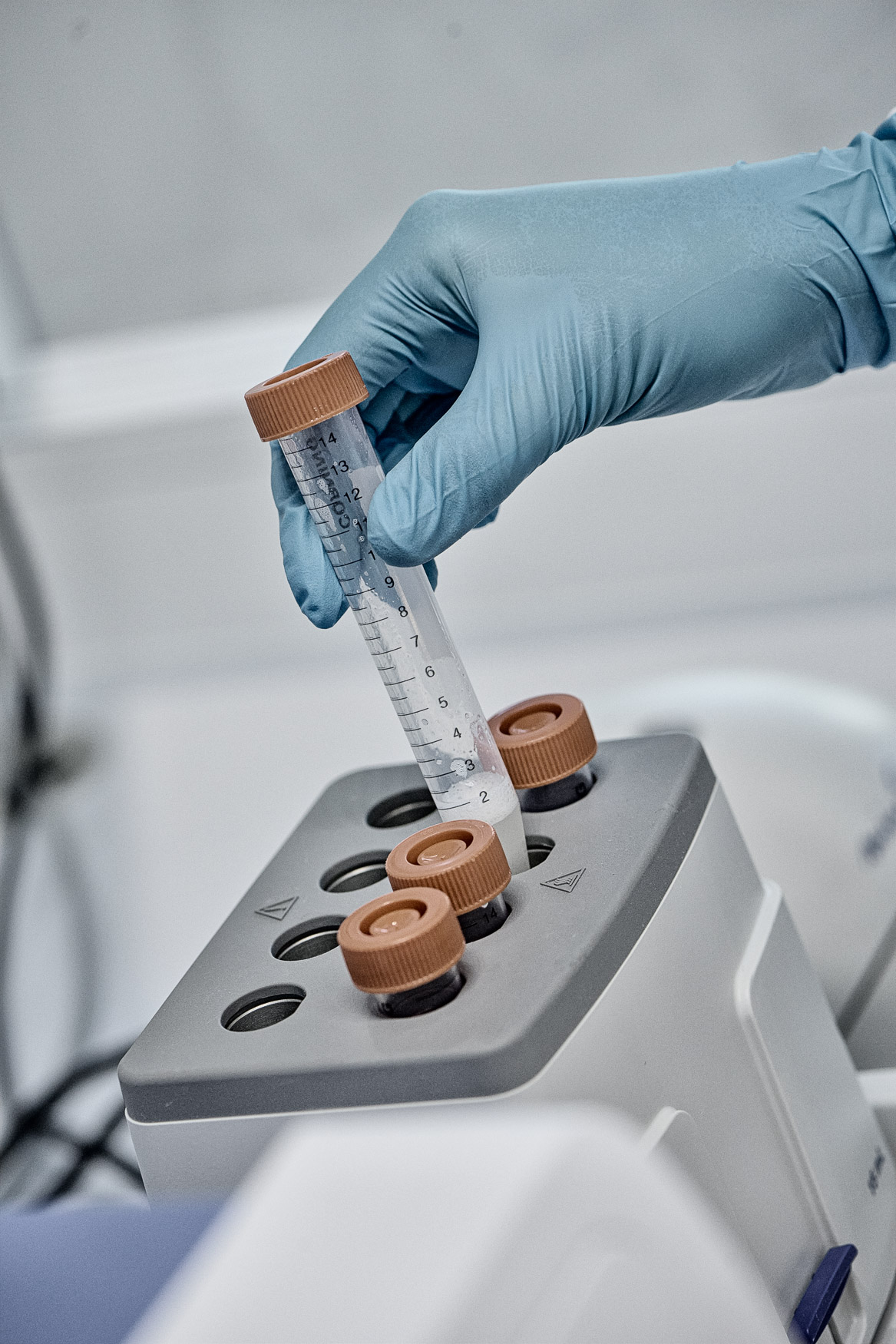
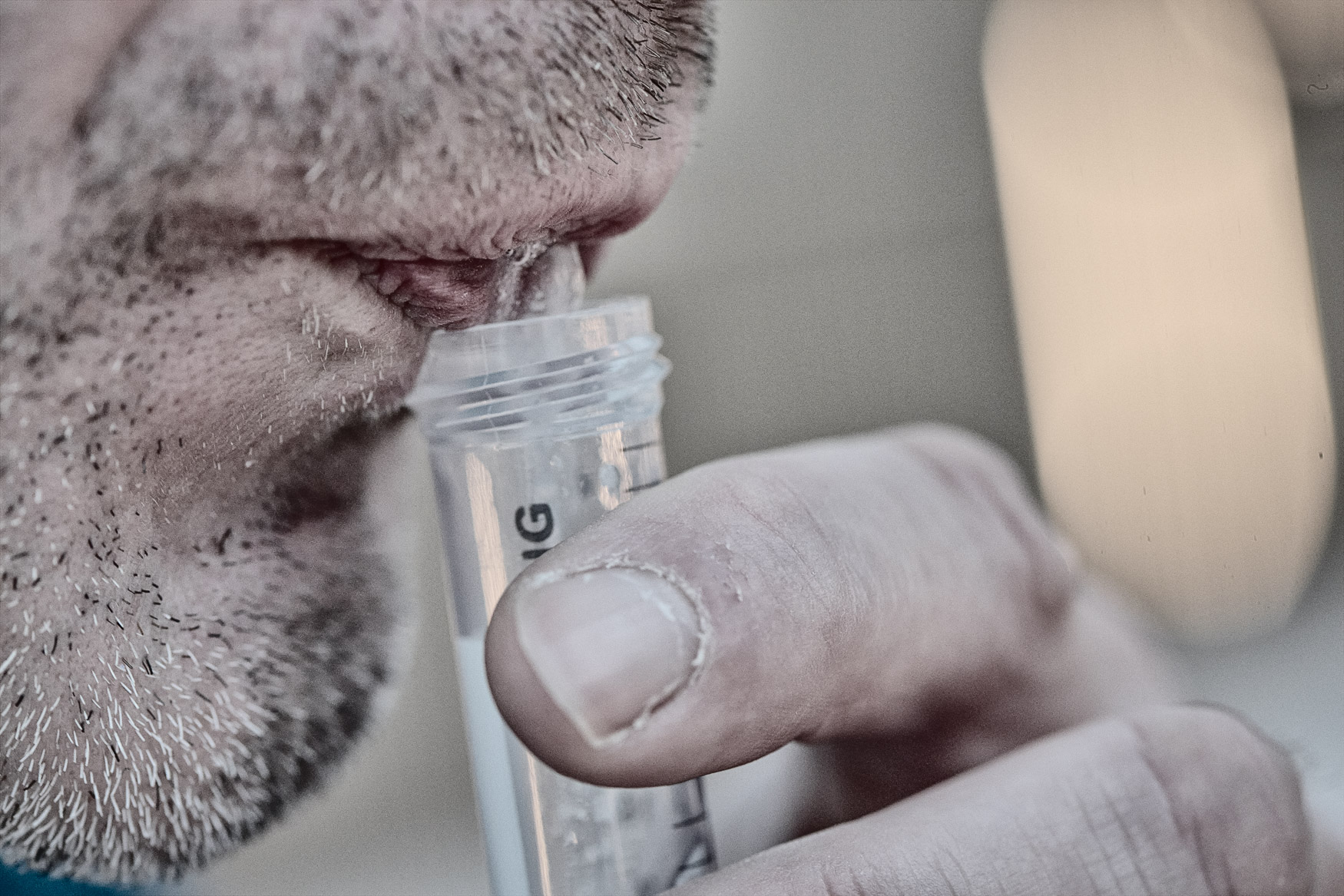
- Monsterafname (neusswab, lastig af te nemen, moet door specialist op specifieke locatie);
- RNA isolatie vanuit monster;
- RT-qPCR test;
- Resultaten verwerken en terugkoppelen.
Tijdens dit projectonderzoek wordt er gekeken om de monsterafname en logistiek te gaan vergemakkelijken. Dit door middel van andere typen materialen te onderzoeken op het Coronavirus i.p.v. de lastig af te nemen neusswab. De mensen die getest moeten worden op het Coronavirus kunnen dat dan zelf doen wat het hele proces makkelijker maakt. Daarnaast worden deze materialen direct getest middels de digitale PCR, een andere meettechnologie dan de RT-qPCR die in het huidige protocol van het RIVM gebruikt wordt. Door gebruik te maken van digitale PCR en een geautomatiseerd uitleessysteem kan er direct uit patiënten samples het Coronavirus worden aangetoond. Hiermee kan de procestijd (sample-to-answer) enorm worden verkort en daarnaast ook de testcapaciteit immens worden vergroot.
Projectdoelstelling/resultaat
- Een analytisch gevalideerde, versnelde en vereenvoudigde moleculaire test voor corona virusdetectie.
- Software of app die het mogelijk maakt dat bijv. huisarts-assistenten de Coronavirus uitslagen makkelijk kunnen inzien en interpreteren (op afstand).
- Mogelijke Businessmodellen met bijbehorende verdienmodellen voor de technische oplossing.
Projectteam
Lectoraat Applied Natural Sciences: Anne Loonen, Joost Schoeber en Juliette Schlaghecke
Lectoraat De ondernemende Regio: Dankeld Vanmeenen
Sure Laboratories: Frank van der Zanden
Scan Europe: Aldo Boon
Goffin Moleculair Technologies: Eric van Vught
Jeroen Bosch Ziekenhuis: Adriaan van den Brule
Afstudeerder FHTNW Applied Science: Anouk Poppelaars
Overige studenten: Nick Voeten, Jeroen Shawgi, Floris Bloemen, Sam van den Einden, Bas Schellekens, Anne Hagens, Beau van de Vossenberg, Baris Demirel, Hugo Merkens, Ergün Incirci, Ruud van der Vleuten, Floor Sluijter, Floor van Merrienboer, Joelle Peters, Lotte Leijer, Famke van Hattem, Ilonka Verschuren, Teun Totté, Marco van den Broek, Jop Heijmans, Mike Peters, Adil Abbaoui, Daphne vd Eertwegh, Bas Wijnhoven, Dennis vd Ouweland, Lucas Heidendaal, Paramithan Jeyarajah, Rinck Vet, Beren Rijksen, Sjoerd vd Heuvel, Robin van den Bommel, Vivian van Hoek
Periode
September 2020 t/m december 2020
Partners
Sure Laboratories
Scan Europe
Goffin Moleculair Technologies
Jeroen Bosch Ziekenhuis
Pers
Pro-motor award 2021 gewonnen door Coronavrije bubbels | Katapult
Coronavrije bubbels in het onderwijs | Eindhovens Dagblad
Hoe kunnen we weer veilig terug naar de campus | Tu/e
Pilot coronavrije communities Eindhovense onderwijsinstellingen | Fontys.nl
Fontys ontwikkelt intelligente teststraat voor coronavrije bubbels op de campus | Bron
Fontys test Corona test zonder keel- en neusswab | AD
Meer geld nodig om veelbelovende pilot met coronatesten succesvol te maken | Scienceguide
Fontys werkt aan coronatest zonder neusswab | omroep Brabant
Fontys oefent met speekseltest | Studio040
Onderstaande foto’s zijn gemaakt in opdracht van PBT voor de promotie van de Pro-motor Award 2021 - zie persbericht Katapult.
Deze mogen niet rechtenvrij gebruikt worden.
Fotograaf: Maarten Noordijk

Dutch Technologie Week: Film van DTW.
Bij minuut 48/49 start het interview.